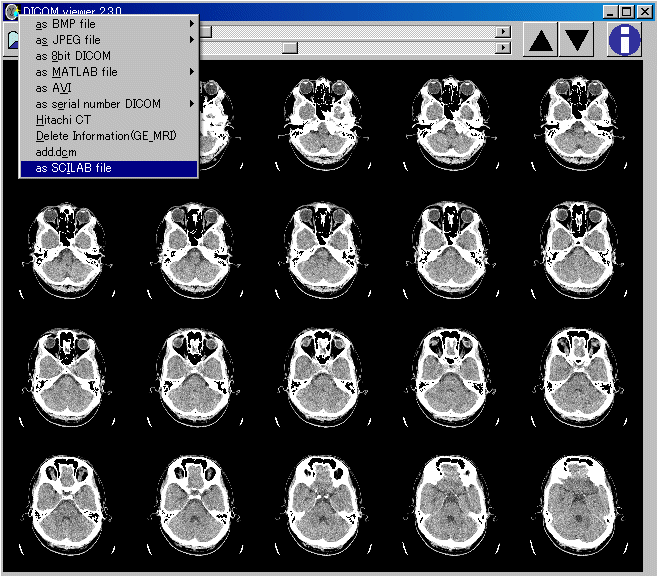
自作フリーウェアのDICOM_viewerを使います。version 2.3.0 以降で対応しています。 尚、このソフトは64x64、128x128、256x256、512x512の画像しか対応していません。 ファイルのアイコンをクリック後に、as SCILAB fileを選択すると、三次元配列のCubeDataという変数名で保存されます。
以後は前述のMRI画像表示と同じです。
load('.../xxx.dat');
B=double(CubeData(:,:,50));
BB=(B-1050)/80*128+128;
BB(BB<1)=1;BB(BB>256)=256;scf();Matplot(BB);
set(gcf(),'color_map',graycolormap(256));
set(gca(),'isoview','on');
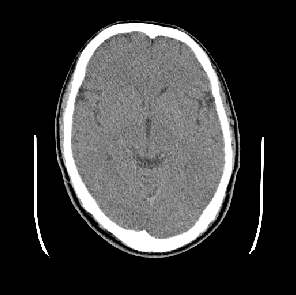
この程度のことであれば通常のDICOM viewerで事足ります。
thresh=1500; Vmax=zeros(CubeData(:,:,1));
for z=1:size(CubeData(:,:,1:50),3);...
Z=double(CubeData(:,:,z));...
Z(Z<thresh)=0;Z(Z>0)=z;...
A=(Vmax<Z);...
Vmax=(Vmax.*~A)+(Z.*A);...
end;
scf();Matplot(Vmax);
set(gcf(),'color_map',graycolormap(50));
set(gca(),'isoview','on');
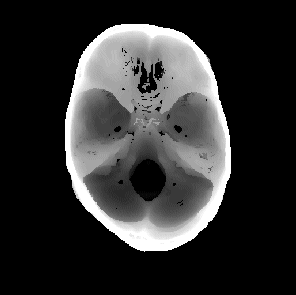
頭蓋底です。
for loopを使うと急激に演算速度が低下します。 stacksizeの制限で512x512x125 boxelのデータを扱うにはもう一工夫要りそうです。