Fiff2MatFileで変換した3次元配列はScilabでは読めません。 そこでMRI画像のあるxxx_3D.fifまたはxxx_3D.scenes.fifをFiff2Sciのversion 1.1.0以降で変換し、 それぞれxxx_3D.datまたはxxx_3D.scenes.datとしたものを読みます。
load('.../xxx_3D.dat'); //file読み込み
B=Volume3D(:,:,50); //Matlabと異なり、自動的に次元が圧縮されるようです
Matplot(B); //画像表示
hf=gcf();hf.color_map=graycolormap(256);//白黒表示
hf.children.isoview='on'; //figure.axes
hf.children.axes_visible='off';
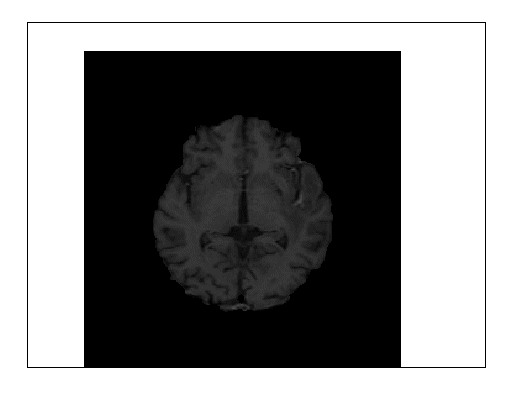
axesの枠はどうも消えません。
視認性を良くするためにwindowレベルとwindow幅を設定してみます。
wl=40;ww=30; //window window & window level
BB=double(B);
BB=(BB-wl)/ww*128+128;
BB(BB<1)=1;BB(BB>256)=256;
scf();Matplot(BB);
set(gcf(),'color_map',graycolormap(256));
set(gca(),'isoview','on');
set(gca(),'axes_visible','off');
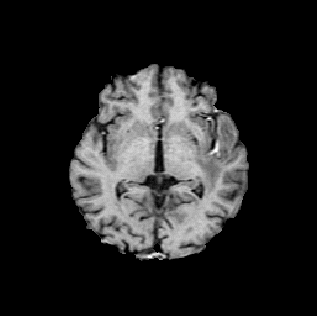
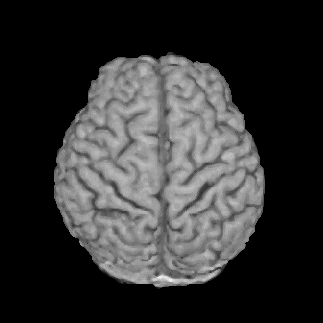
同様にxxx_3D.scenes.datもみてみます。
load('.../xxx_3D.scenes.dat');
B=Volume3D(:,:,10);
scf();Matplot(B);
set(gcf(),'color_map',graycolormap(256));
set(gca(),'isoview','on');
set(gca(),'axes_visible','off');
windowレベル、window幅を変えるときは上記に倣ってください。