内容
MRIcronでNIfTIファイル作成
MRIcronのdcm2niiを使ってDICOMファイルをNIfTIファイルに変換します。
MRIcronはWindows版、Mac版、Linux版があります。
ここではLinux版について説明します。
Ubuntu 12.04を使います。
<dcm2niiのあるフォルダ>/dcm2nii <DICOMファイルのあるフォルダ>
でNIfTIファイルに変換されます。
端末はCtrl+Alt+Tで開きます。
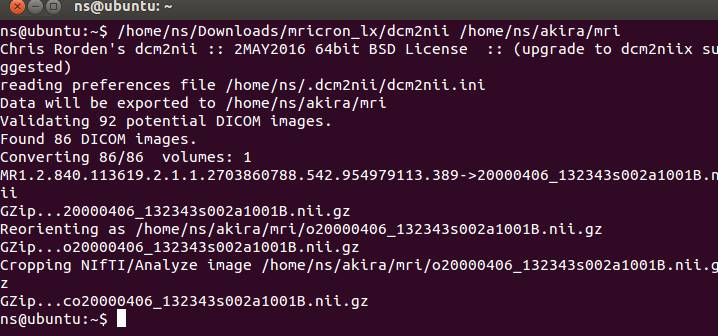
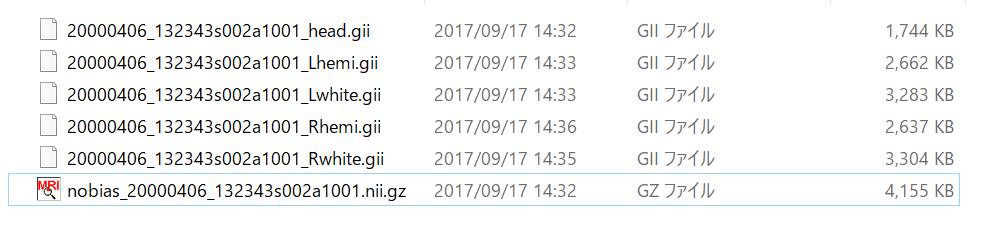
DICOMファイルのあるフォルダに3つのファイルが作成されます。nii.gzは圧縮NIfTIファイルを示す拡張子です。
coとかoがついてないnii.gzファイルを使うことにします。
図は別途導入したFile Browser Marlinで表したものです。
BrainVISAの準備
2回目からはこの過程は省略してください。
端末を開き
/opt/brainvisa/BrainVISAでBrainVISAを起動します。
Open preferencesをクリックします。
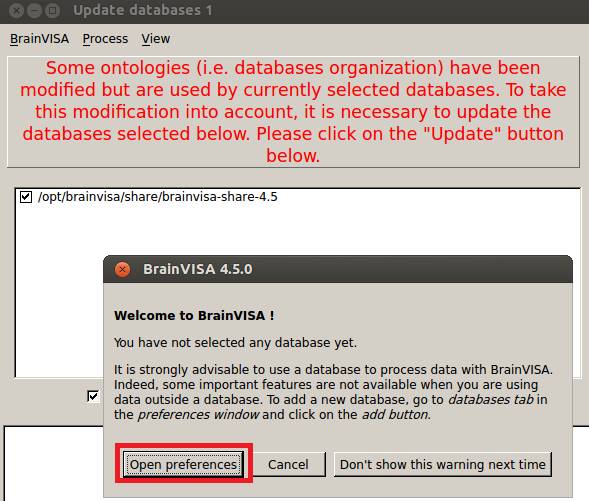
BrainVISAのuserLevelをExpertにします。
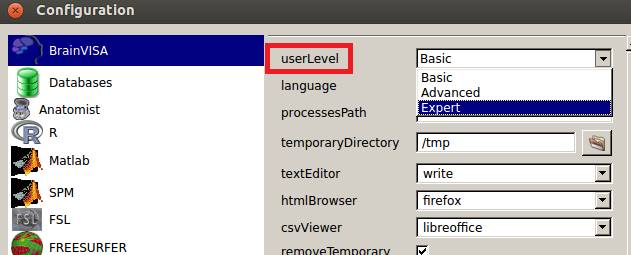
BrainVISA用のデータベースを作成します。Databasesをクリックし、Addでデータベース用のフォルダを指定し、チェックを入れます。よければOkを押します。
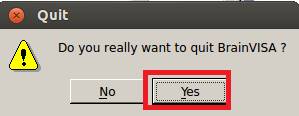
BrainVISAをいったん終了します。
Yesを押します。
BrainVISAのデータベースにNIfTIファイルを登録
BrainVISAを再起動し、チェックを先ほど作成したデータベースフォルダのみにし、Updateをクリックします。
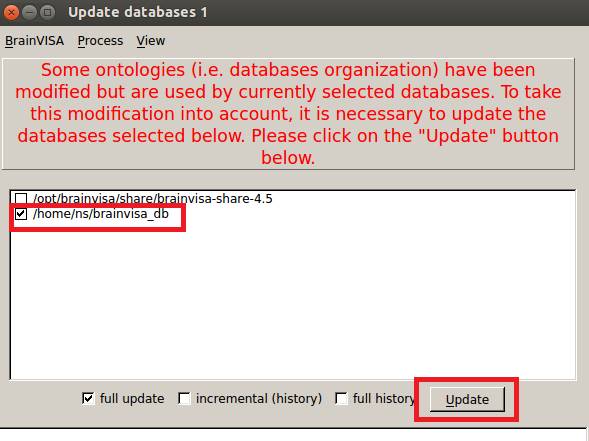
![]() をクリックしてウインドウを閉じます。
をクリックしてウインドウを閉じます。
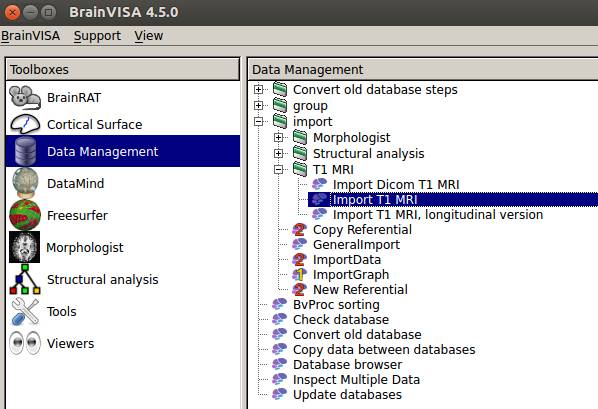
Data Managementをクリックし、import→T1 MRI→Import T1 MRIをダブルクリックします。
Import T1 MRIウインドウが開きます。
![]() をクリックして、先ほど作成したNIfTIファイルを選択し、Runを押します。
をクリックして、先ほど作成したNIfTIファイルを選択し、Runを押します。
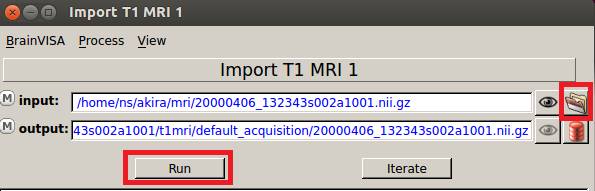
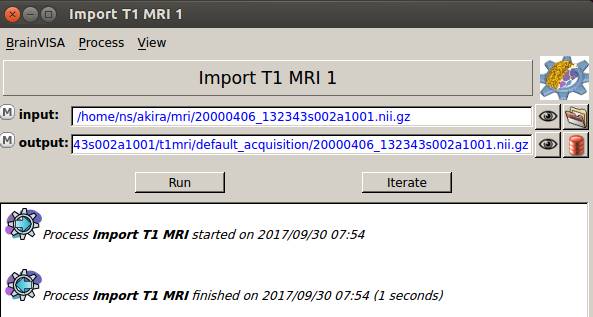
BrainVISAのデータベースにNIfTIファイルが登録されました。
Import T1 MRIウインドウは閉じます。
BrainVISAで脳の切り出し・メッシュ化
MorphologistのMorphologist 2015をダブルクリックします。
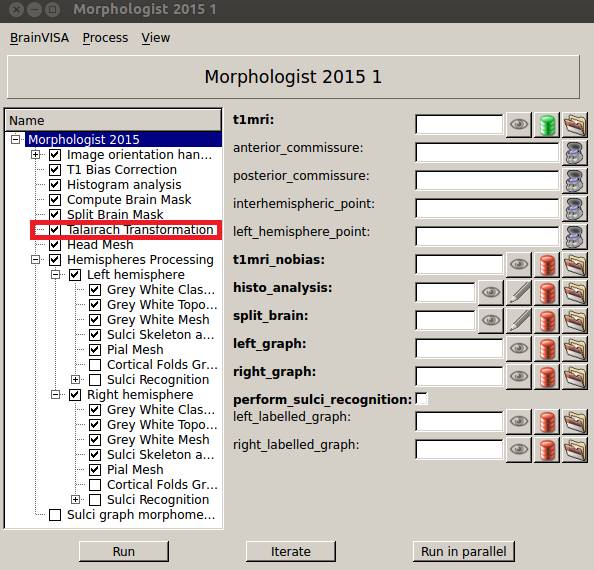
Talairach Transformationにチェックを入れます。Cortical Folds・・・のチェックは不要です。
![]() をクリックし、登録したRaw T1 MRIを選択し、Okを押します。
をクリックし、登録したRaw T1 MRIを選択し、Okを押します。
![]() を押すとAnatomistが起動します。
を押すとAnatomistが起動します。![]() で断面を選択します。
で断面を選択します。
カーソルを前交連に合わせ、![]() を押します。
を押します。
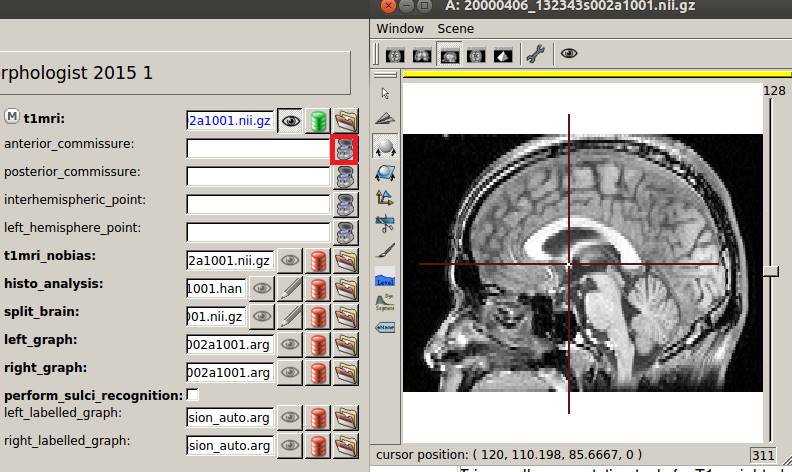
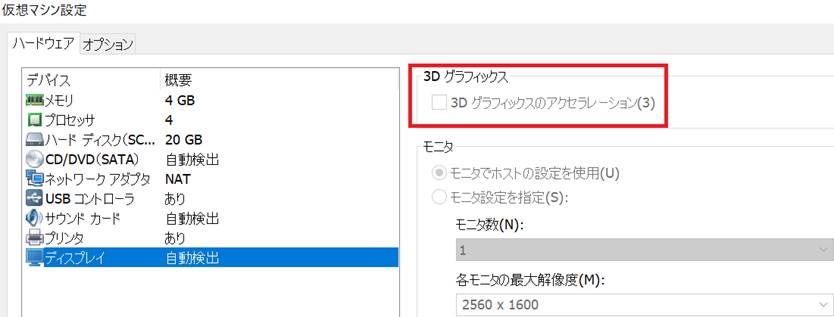
もしカーソル位置が画像末端になる場合はVMwareの3Dグラフィックスの3DグラフィックアクセラレーションがOFFになっていることを確認してください。
前交連の座標が取得されます。
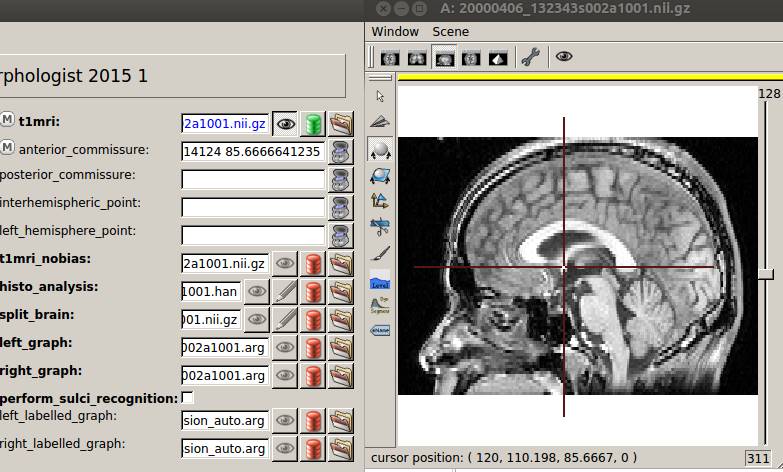
同様に後交連、大脳半球間裂、左大脳半球の座標を取得します。
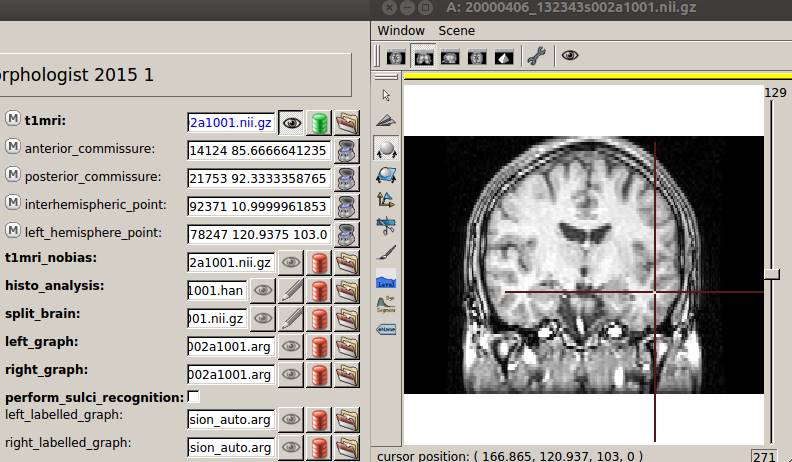
Run in parallelをクリックします。
OKを押します。
(並列)処理が進行します。
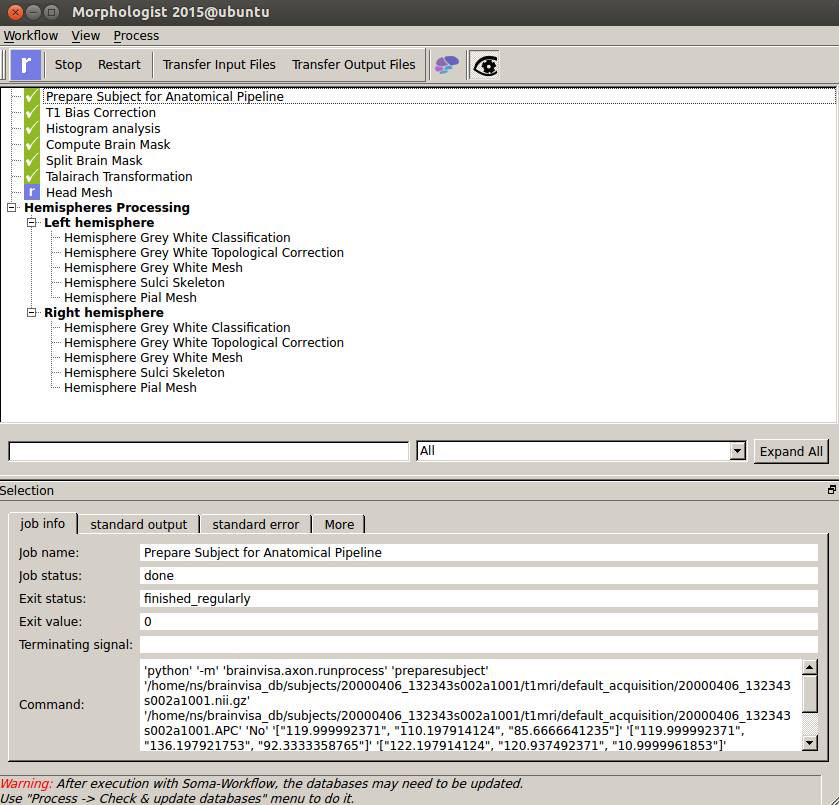
処理が終わりました。このウインドウを閉じます。
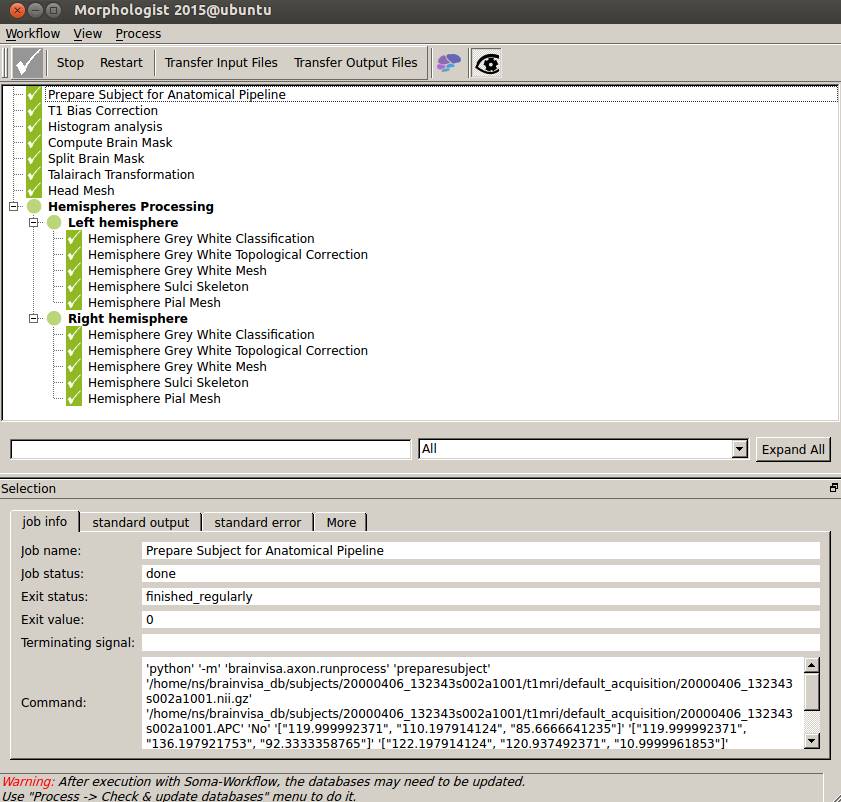
Cortical Folds Gr…をクリックし、white_mesh:とpial_meshの![]() をクリックし、メッシュが表示されたら成功です。
をクリックし、メッシュが表示されたら成功です。
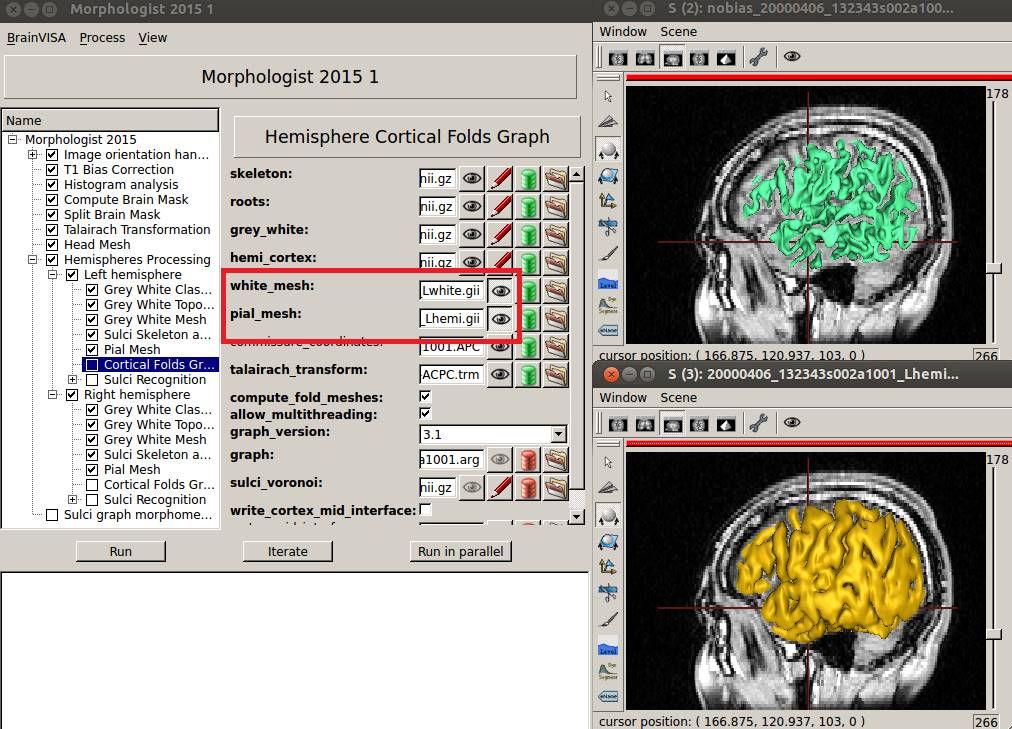
これでBrainVISAでの処理は終了です。
メッシュ・画像・脳磁図ファイルの選択
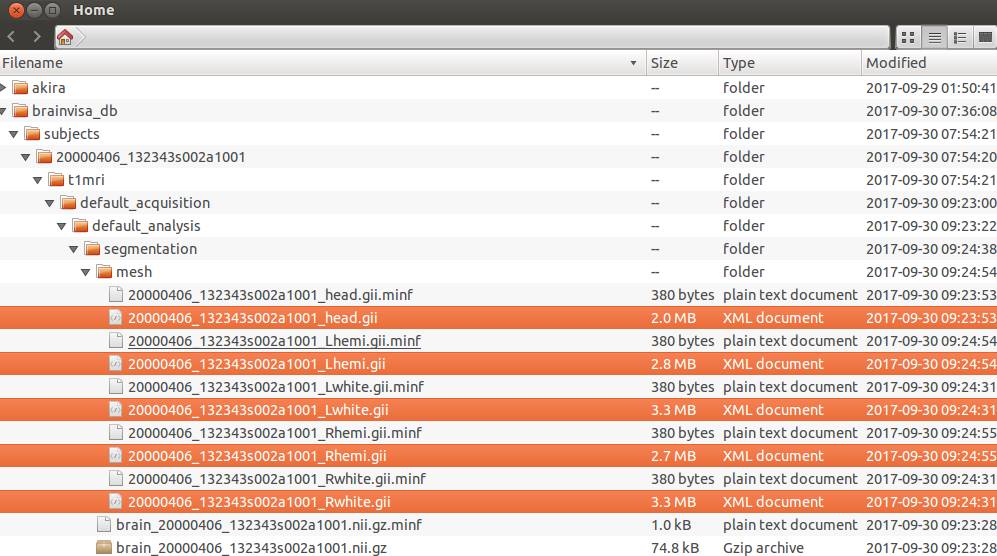
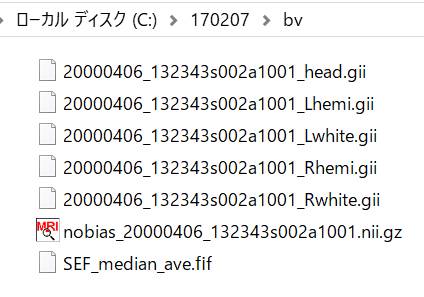
とりあえず以下の6つのファイルをコピーしてみます。
頭皮メッシュファイル、〇〇_head.gii
左右半球皮質のメッシュファイル、〇〇_Lhemi.giiとRhemi.gii
左右皮髄境界のメッシュファイル、〇〇_Lwhite.giiとRwhite.gii
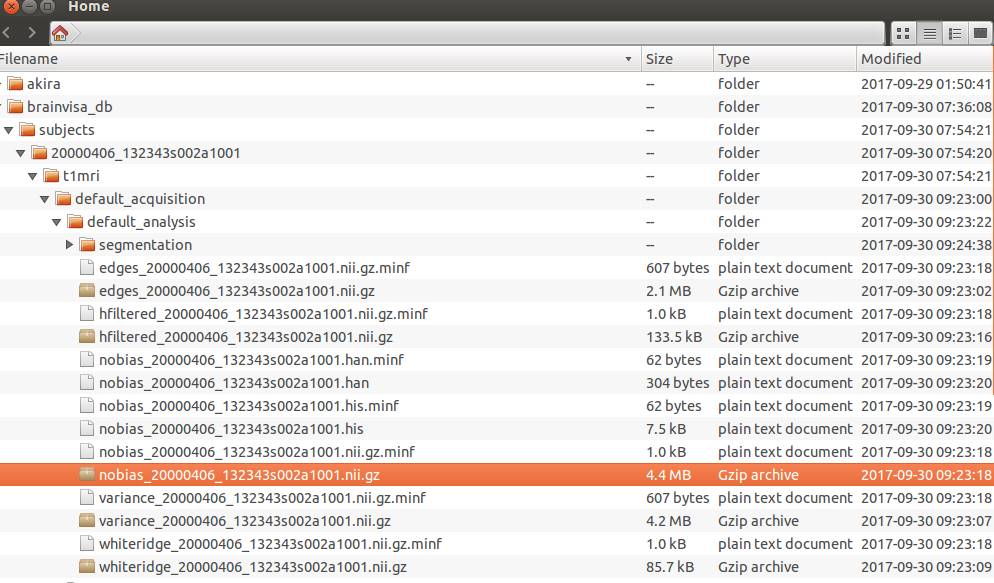
MRIの三次元配列データ、nobias_〇〇.ni.gz
〇〇inflated.giiは必要ありません。
〇〇hemi.giiは皮質に電流源を置く場合、〇〇white.giiは皮髄境界に電流源を置く場合です。どちらか一方があればOKです。
giiファイルの場所は以下の通り。
nii.gzファイルの場所は以下の通りです。
Windows側の適当に1つのフォルダに入れておきます。
〇〇.nii.gzファイルはMRIcroで開くようにしているのでアイコンが![]() になっています。
になっています。
脳磁図データもついでに入れておきます。右正中神経電気刺激の体性感覚誘発脳磁場の加算波形です。
BrainStormに登録
BrainStormはWindowsで起動したものとしますが、基本MatlabベースなのでLinux、Macでもほぼ同じ操作になるはずです。。
File→New Subjectを選択します。
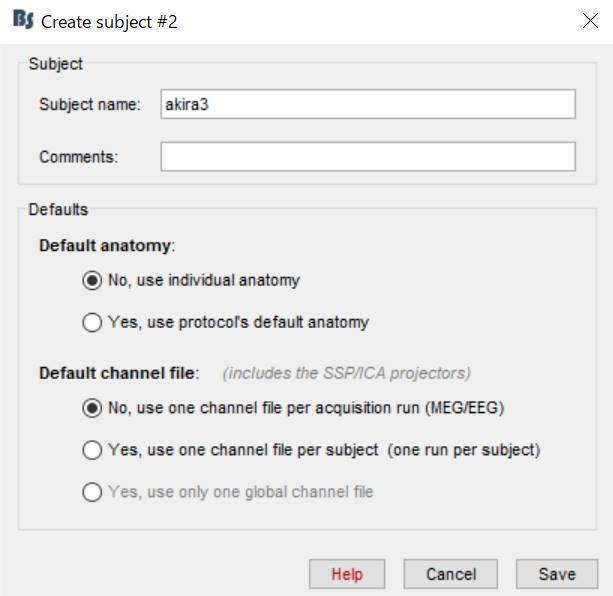
Subject name:をakira3としSaveを押します。
akira3を右クリックしImport MRIを選択し、NIfTI化したMRIの元ファイル、nobias_〇〇.nii.gzを選びます。
はい(Y)を選択します。
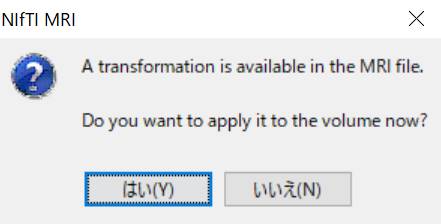
鼻根点、左右耳珠、前交連、後交連、半球間裂を指定し、Saveを押します。
MRIが登録されました。
akira3を右クリックしてImport surfacesをクリックします。
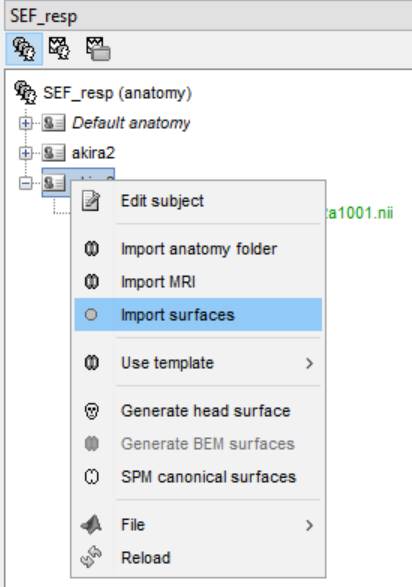
giiファイルを全部選択します。
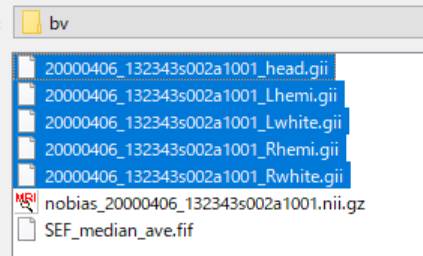
いいえ(N)を押します。
メッシュファイルが登録されました。
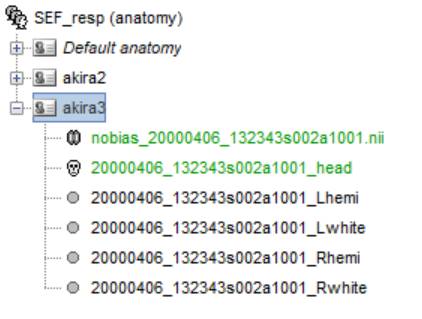
このままでは重いのでメッシュ頂点の数を約15,000個、左右半球で7,500個にします。
左右半球のメッシュを選んで右クリックします。
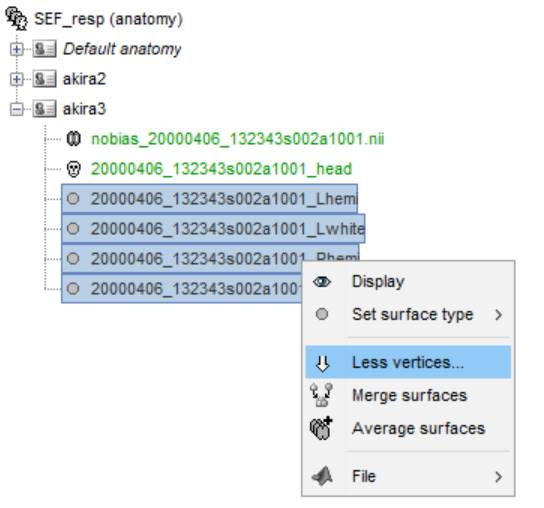
7500個にします。
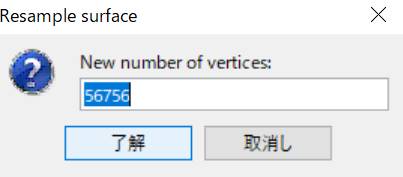
7500個に変更後、了解を押します。
了解を押します。
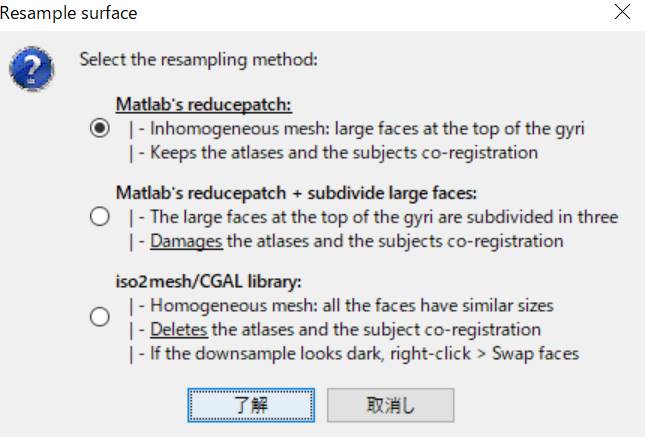
頂点数が約7500個になったメッシュが作成されました。
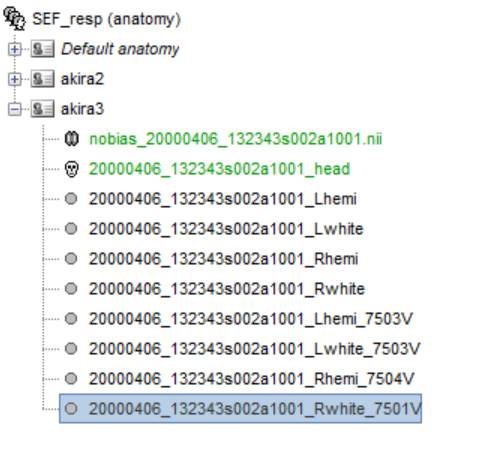
左右のhemiを選択し、右クリック後、Merge surfacesを選択します。
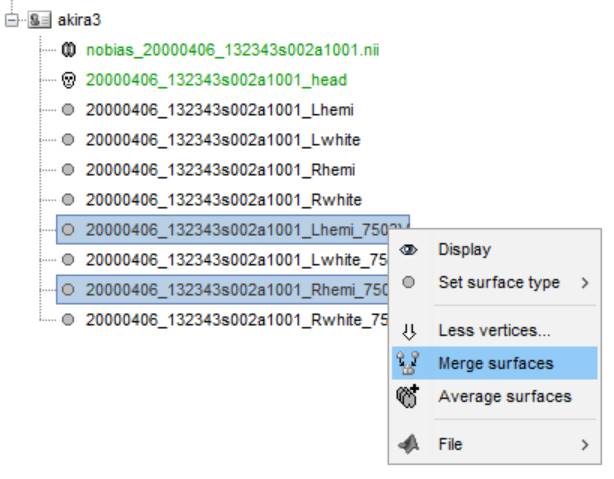
cortexが作成されました。
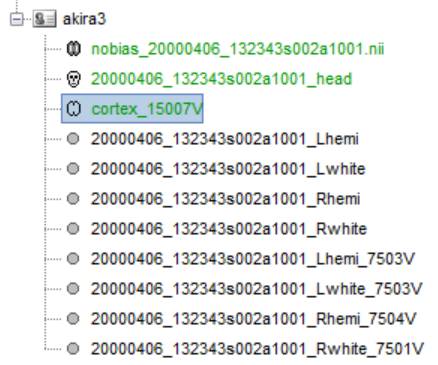
左右のwhiteを選択し、右クリック後、Merge surfaceをクリックします。
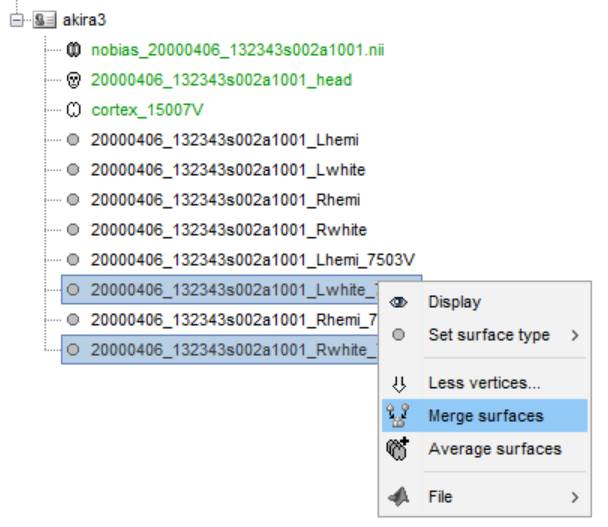
whiteが作成されました。cortexかwhiteを皮質として登録できます。登録した方が緑色で表示されます。
登録した方に電流源をおいて電流源推定をすることになります。
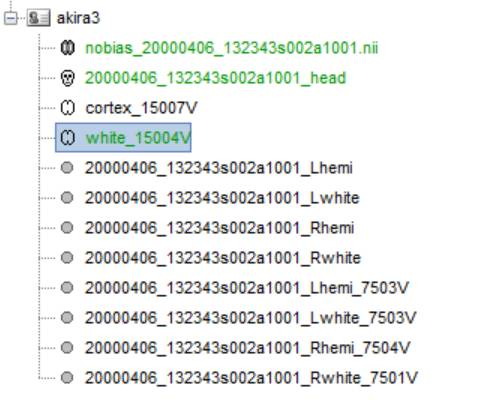
cortexを皮質として登録する場合はcortexを右クリックし、緑のSet as default cortexとします。
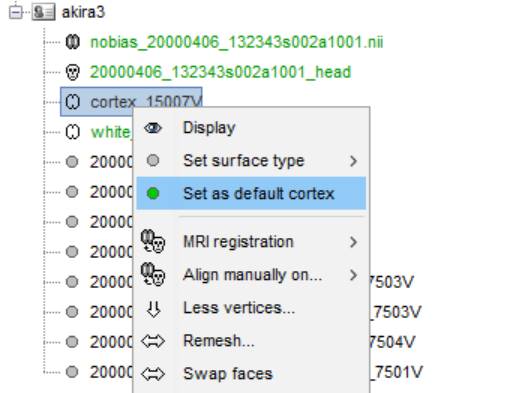
cortexが菱っとして登録されました。
whiteを皮質として登録しなおします。
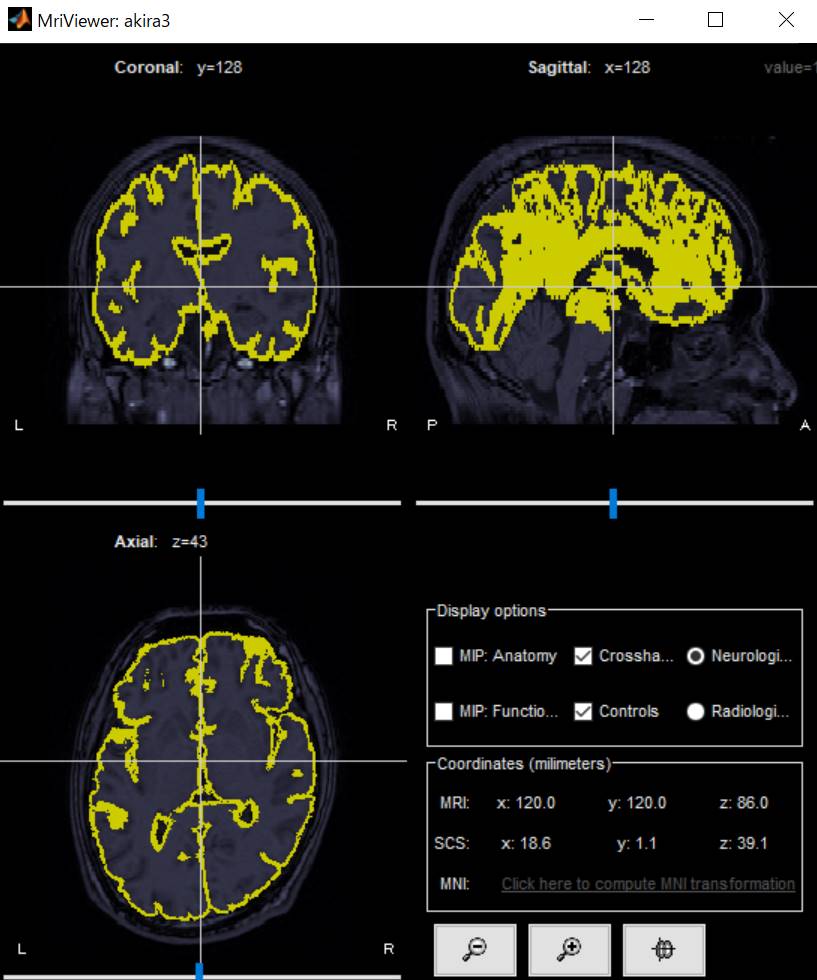
cortexを右クリックし、MRI registration→check MRI/surface registrationを選びます。
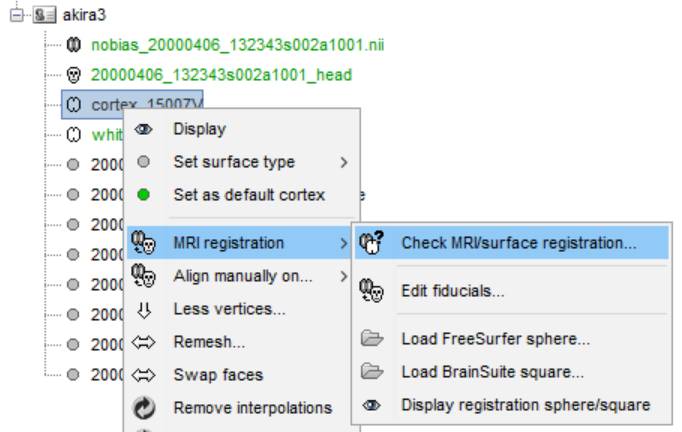
ちゃんと皮質を抽出できているようです。
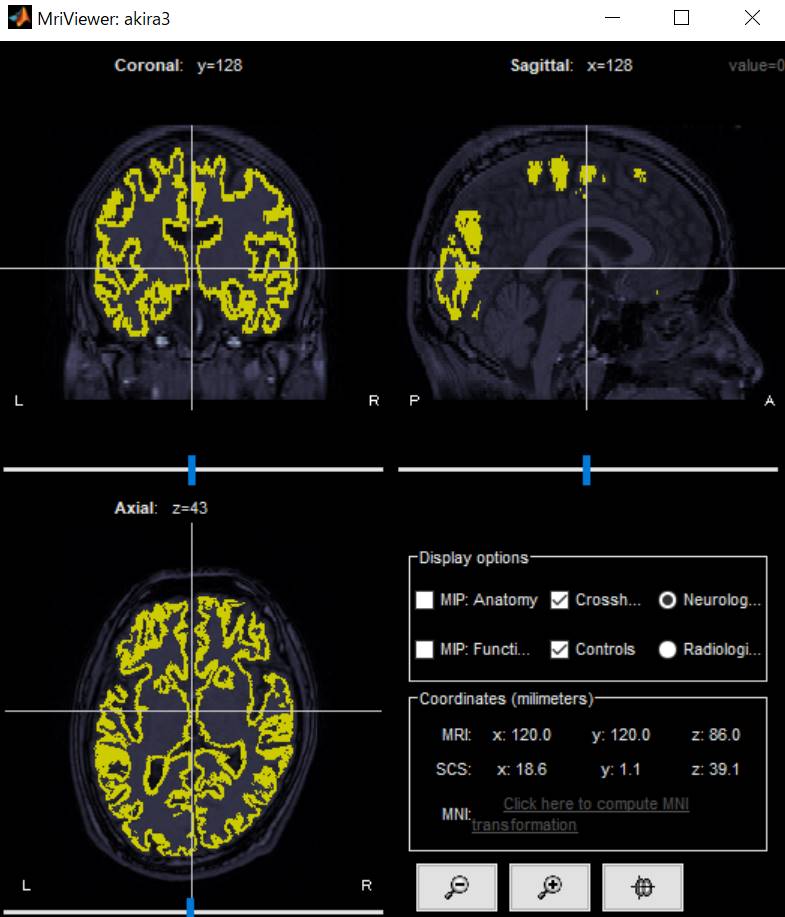
whiteでやった場合です。
cortexを右クリックし、Displayを左クリックします。
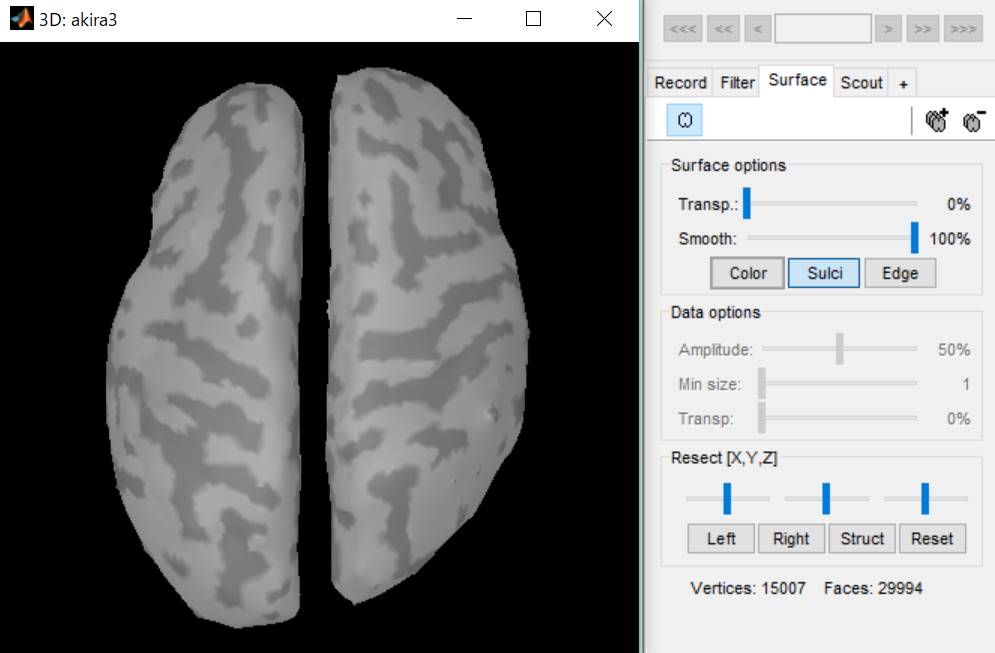
Sulciをクリックし、Smooth:を100%にします。
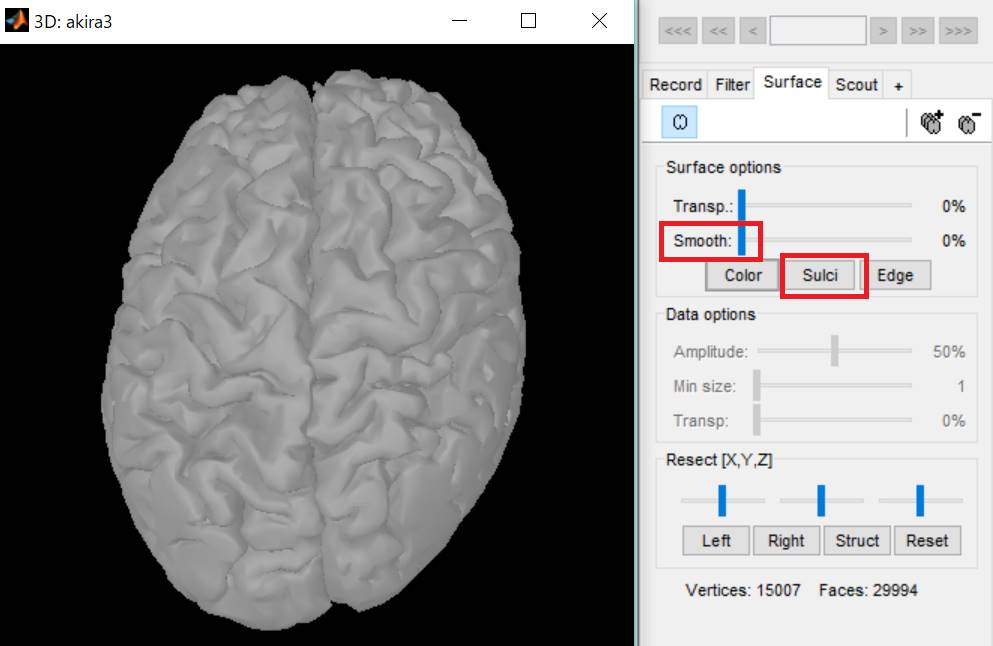
ちゃんと膨らみました。
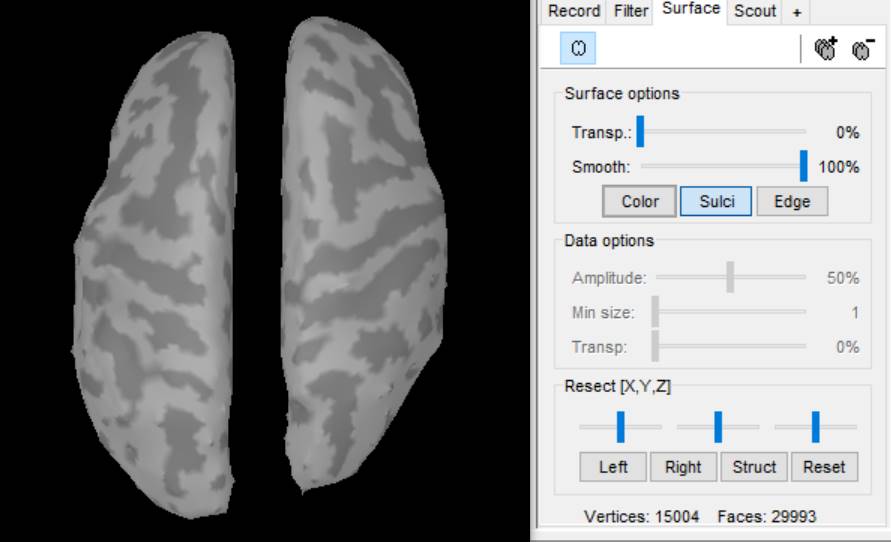
皮髄境界whiteを表示してみました。Sulciを押し、Smooth:100%にしてみます。
こちらでもちゃんと膨らんでいます。
脳磁図データの読み込みと座標合わせ
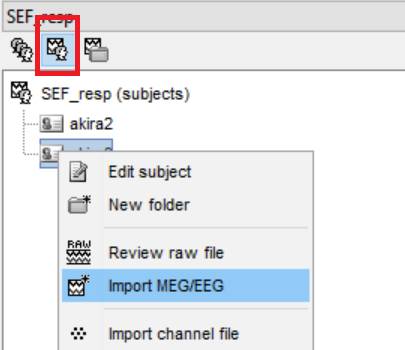
![]() を選択し、akira3を右クリックしImport MEG/EEGを選択します。
を選択し、akira3を右クリックしImport MEG/EEGを選択します。
ファイルタイプを*.fifにしてファイルを開きます。
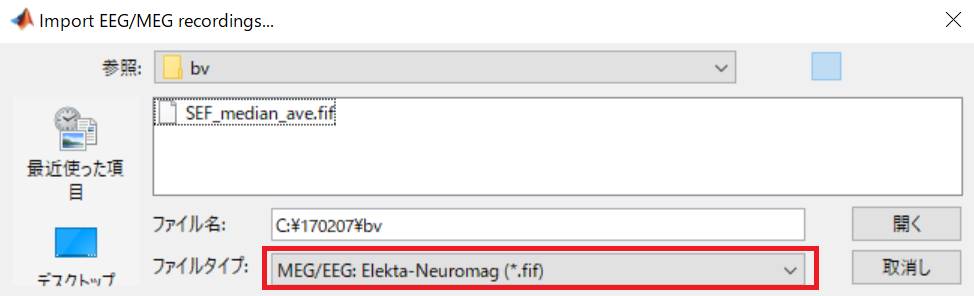
DC offsetにチェックを入れてもいいですが、そのままImportすることにします。
はい(Y)をクリックします。
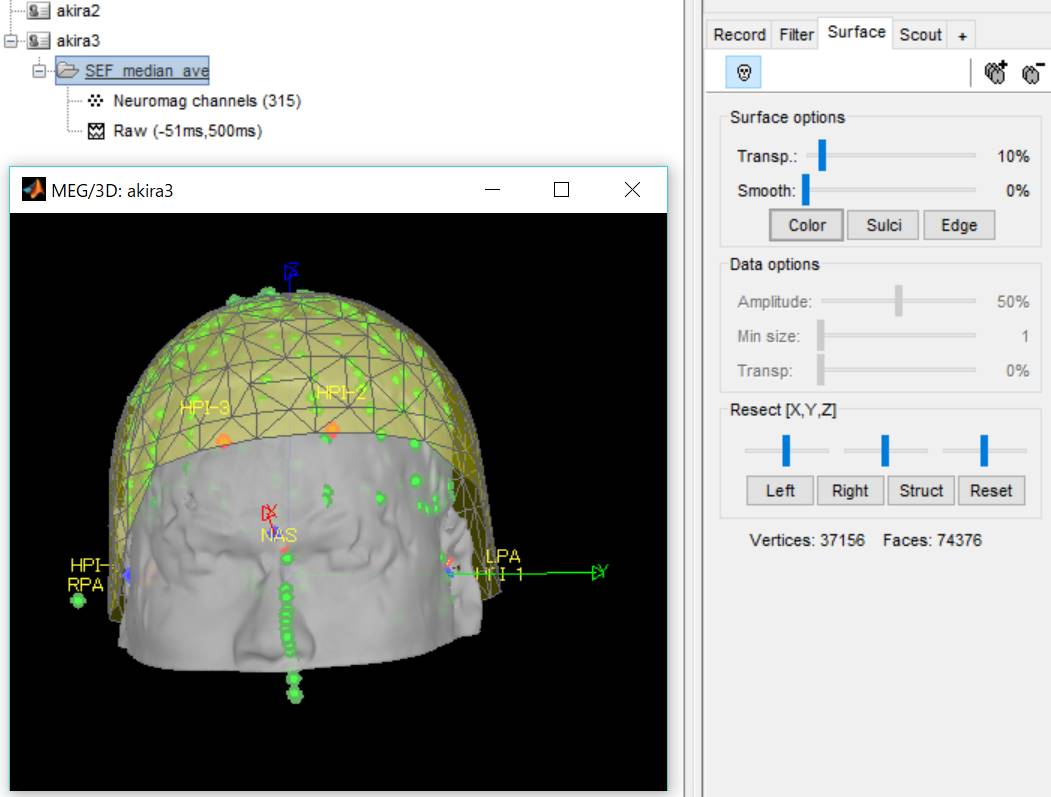
脳磁図ファイルが登録され、頭皮メッシュとPolhemusで登録したHPIの点が表示されます。
この時点でHPIの頭座標とMRIの座標合わせは行われていません。
Neuromag channelsを右クリックしMRI registration→Edit…を選択します。
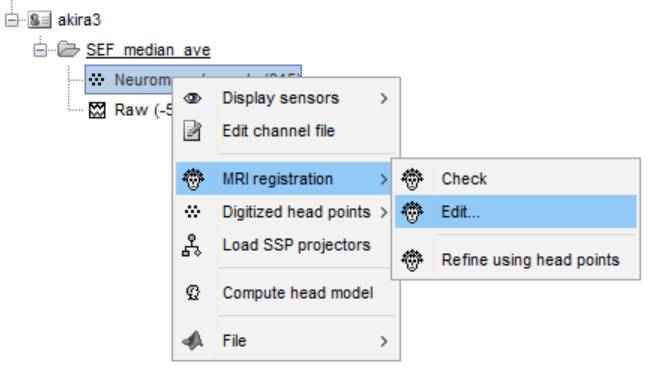
![]() Dewarを非表示にし、
Dewarを非表示にし、![]() でHPI点を平行移動させ、
でHPI点を平行移動させ、![]() でHPI点を回転移動させます。よければOKを押します。
でHPI点を回転移動させます。よければOKを押します。
X軸が前後方向、Y軸が水平方向になっています。
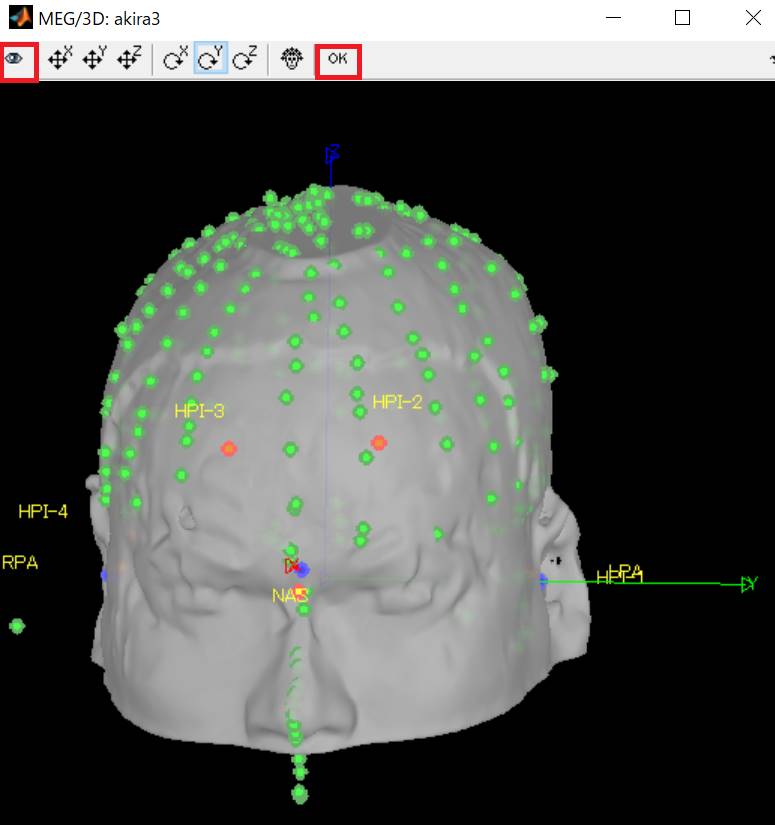
はい(Y)をクリックします。
波形の信号処理
波形をドラッグし、![]() を選択し、
を選択し、![]() をクリックします。
をクリックします。
![]() をクリックし、Pre-process→Band-pass filterを選択します。
をクリックし、Pre-process→Band-pass filterを選択します。
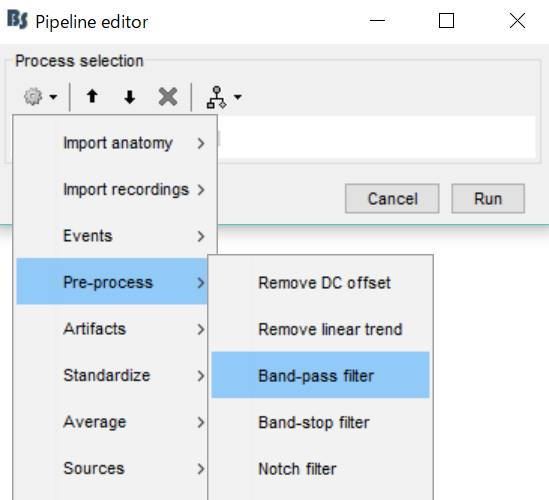
2-100Hzにしてをクリックします。
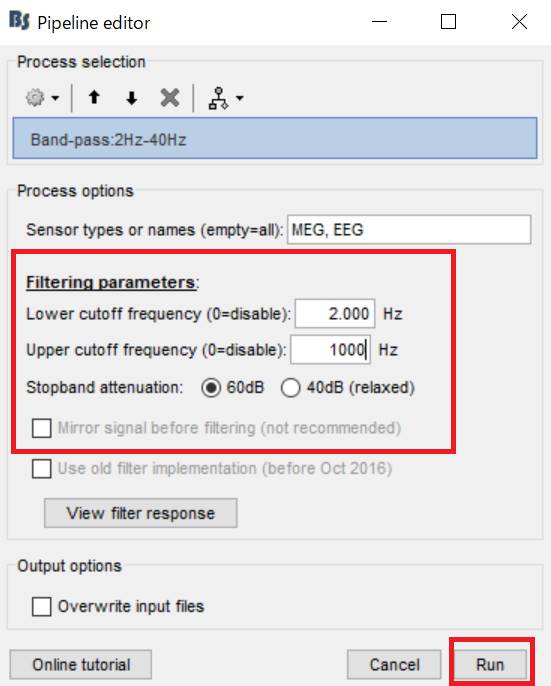
ウインドウを閉じます。
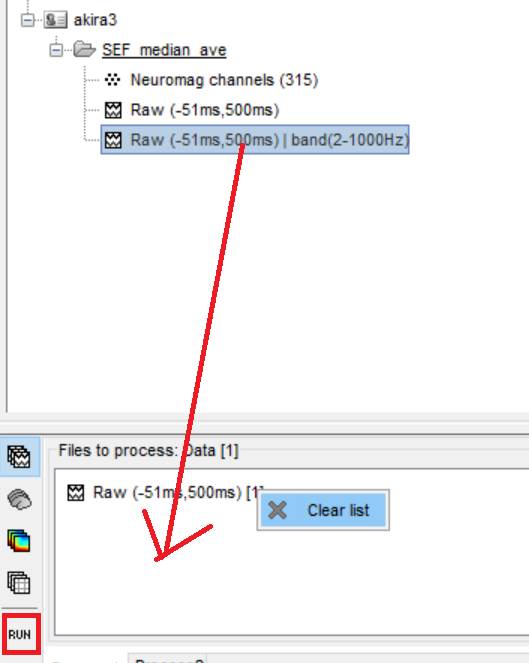
Files to be process:のファイルを右クリックしてClear listとし、周波数フィルタ処理済みのデータをドラッグし、RUNを押します。
Pre-process→Remove DC offsetを選択します。
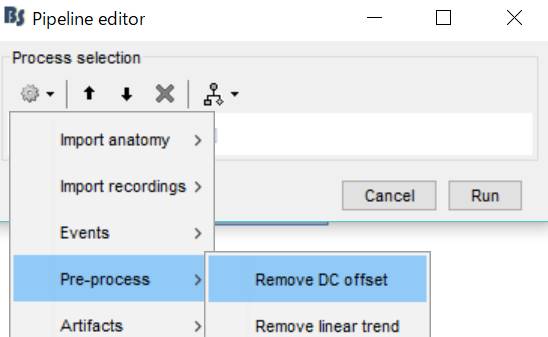
Runをクリックします。
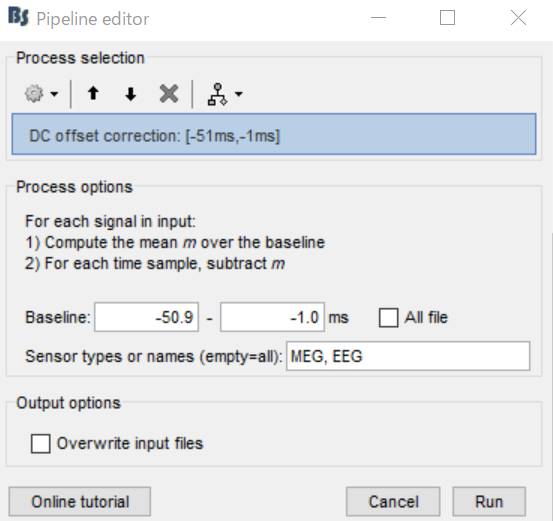
base line補正のデータができました。
電流源推定
Neuromag channelsを右クリックし、Compute head modelを選択します。
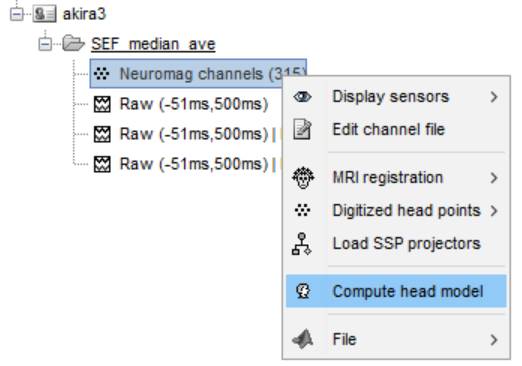
皮髄境界whiteを皮質に登録しているので、皮髄境界に電流源がおかれます。OKを押します。
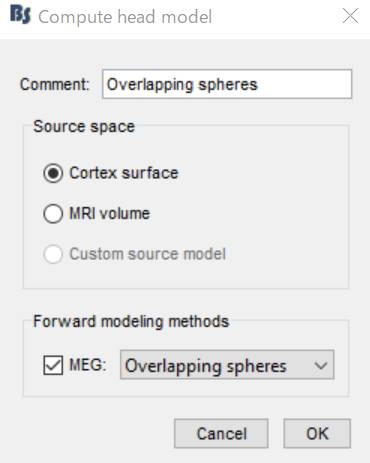
Overlapping spheresが計算されます。
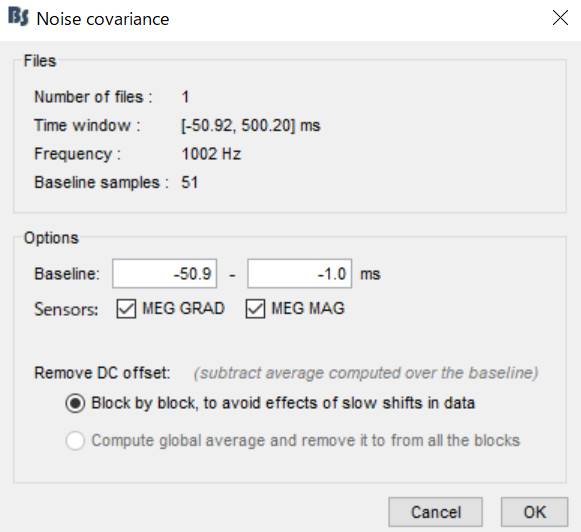
フィルタ処理+ベースライン補正後のデータを右クリックし、Noise covariance→Compute from recordingsを選択します。
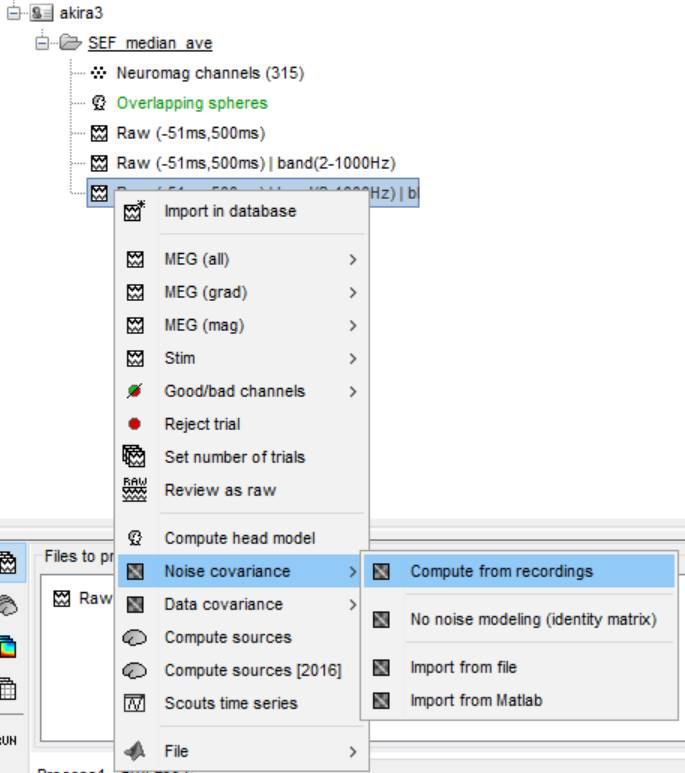
OKを押します。
フィルタ処理・ベースライン補正データを右クリックしCompute sourcesを選択します。
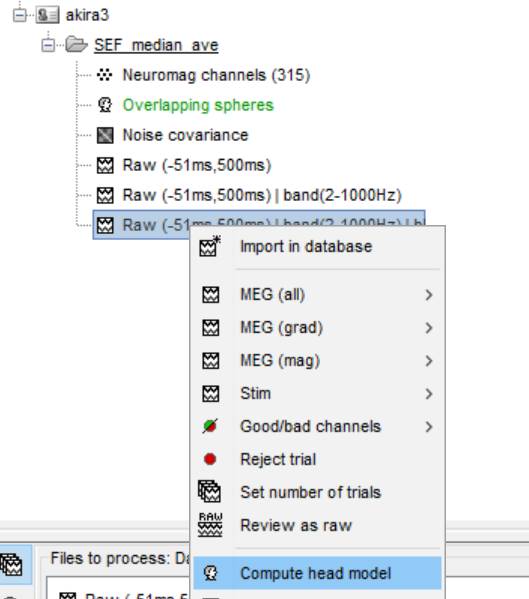
OKを押します。
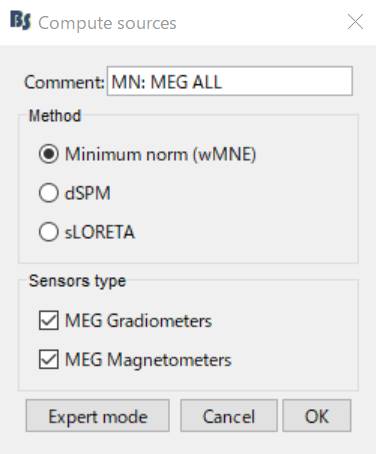
計算されたMN:MEG ALLを右クリックし、Cortical activations→Display on cortexを選択します。
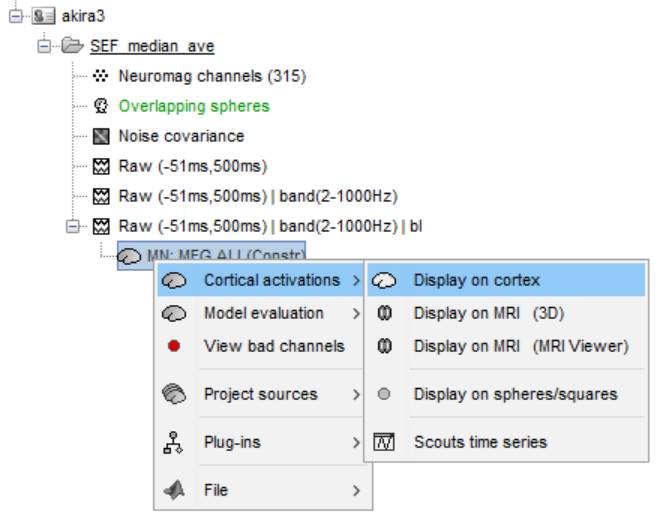
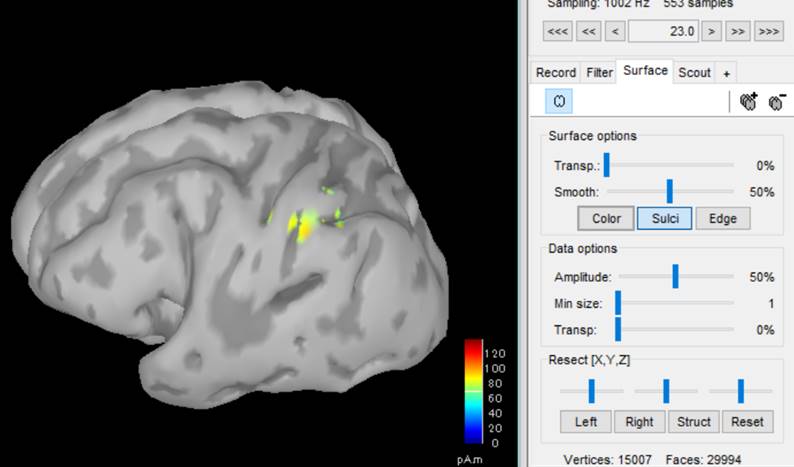
Smoothを50%にし、23.0msの脳活動を表示させています。
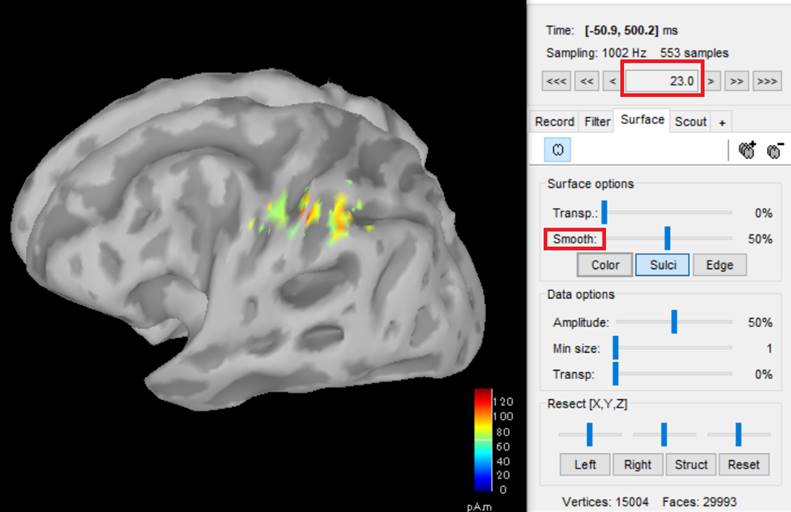
皮質表面cortexに電流源を置いた場合です。微妙に電流分布が異なっています。