BrainStorm
BrainSuiteで作成した脳の3Dデータと皮質メッシュデータをBrainStormで使えるかどうか試しました。
結論はそのまま使えました。
準備
MATLAB R2018b 64bit Windows版を起動します。
BrainStorm3 07-Mar-2019版を起動します。
SEFというプロトコルを作成します。
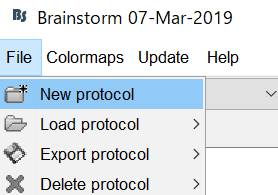
SEFという名前にします。
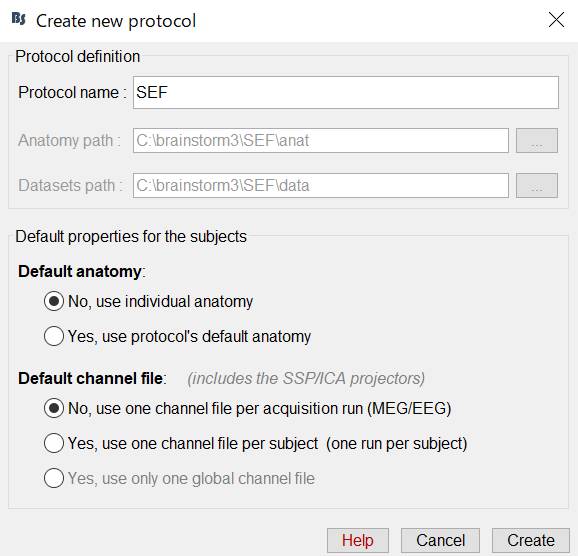
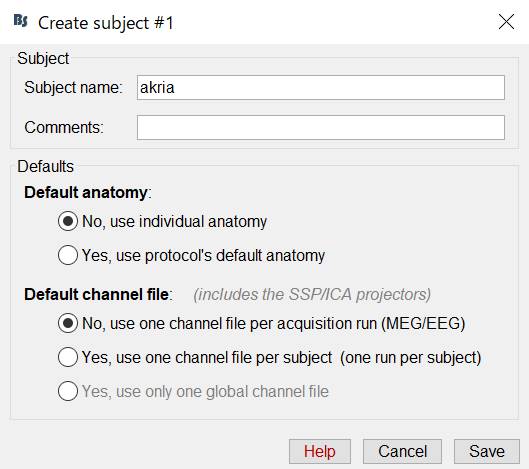
SEF (anatomy)を右クリックし、New subjectを作成します。
akiraという名前にします。
脳画像データとメッシュデータの読み込み
akiraを右クリックしImport MRIを選択します。
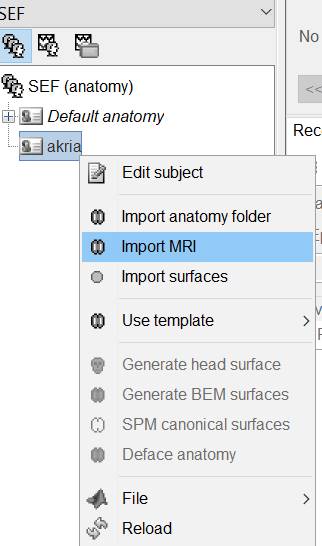
DICOMからNIfTIに変換しただけの〇〇.nii.gzファイルを選択します。
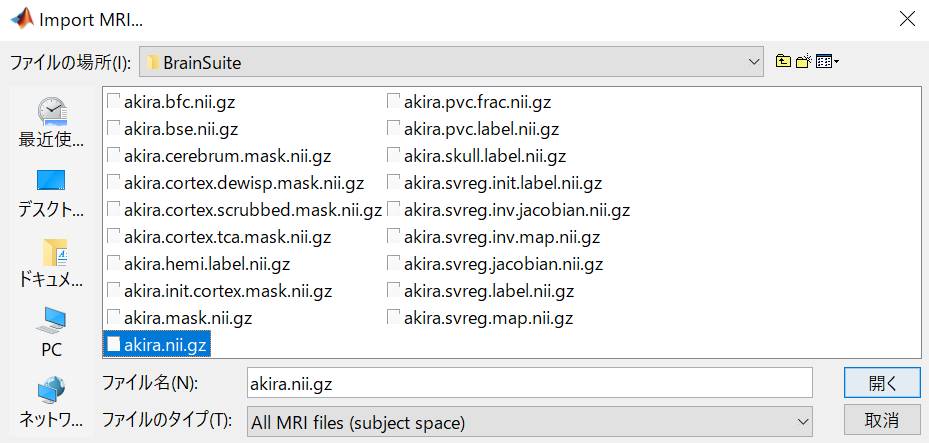
はいを選択します。
鼻根点、左右耳珠、前交連、後交連、半球間裂を指定します。
akiraを右クリックしてImport surfacesを選択します。

〇〇.pial.cortex.dfsを選択します。
はいを押します。

akira.pial.cortexを選択し、Check MRI/surface registration...を選択します。
なお、この過程は省いてもかまいません。確認だけです。
皮質表面がちゃんと黄色になっていることが確認できました。
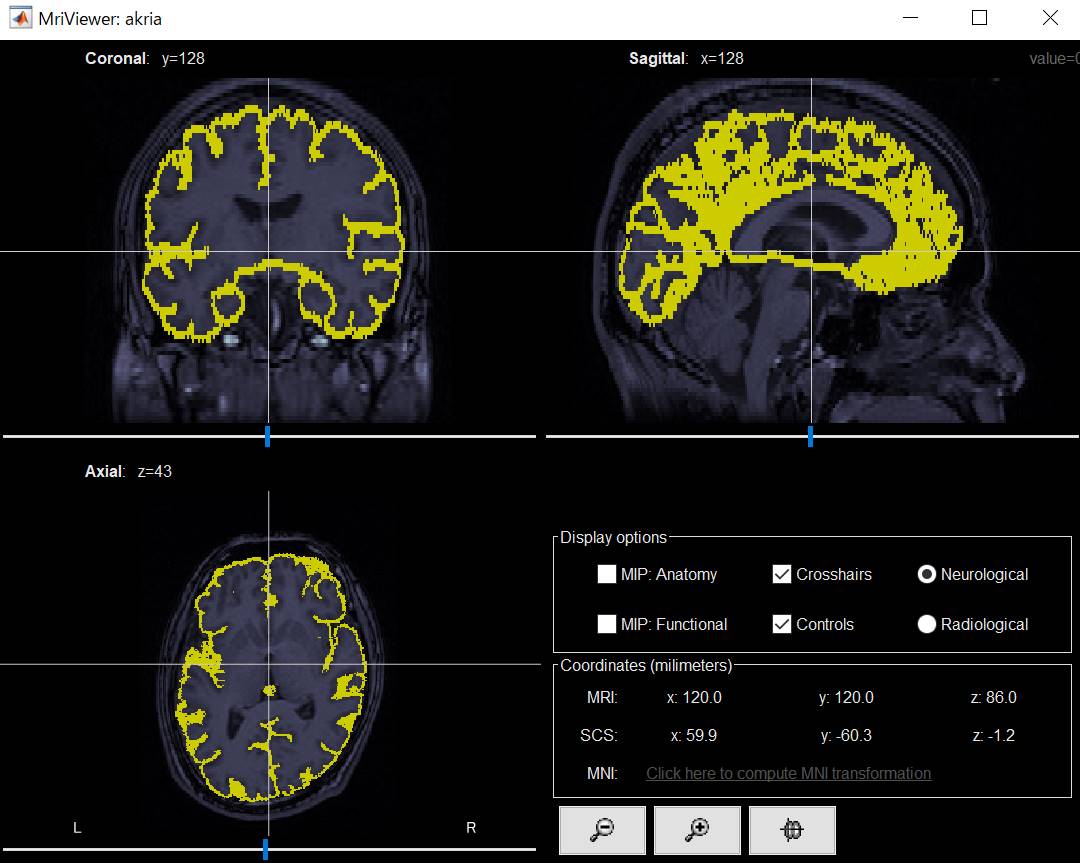
確認後画面を閉じます。
演算量節約のため〇〇.pial.cortexの頂点数・メッシュ面数を減らします。
akira.pial.cortexを右クリックし、Less vertices...を選択します。
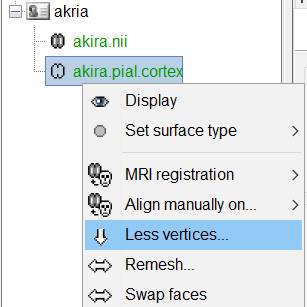
頂点数17万余を15000にしてOKを押します。

頂点数削減法の選択ができますが初期値とします。OKを押します。
表示させてみます。右クリックでDisplayを選択します。

表示されました。
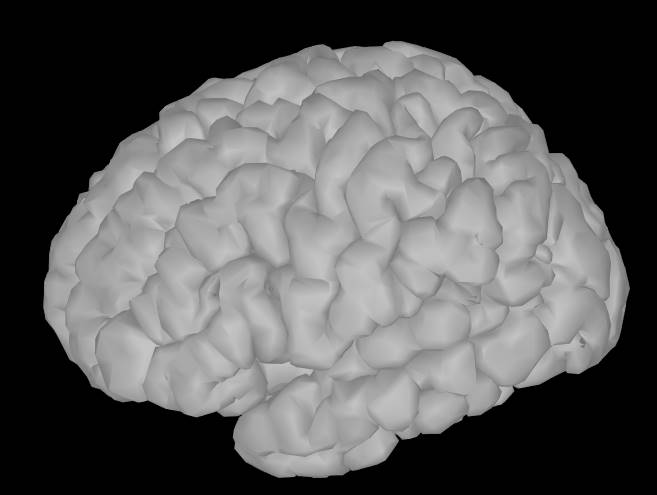
SulciをオンにしてSmoothを80%にします。

見慣れた絵が出てきました。
頭皮メッシュも読み込みます。メッシュ数は15000に減らします。
〇〇.scalp.dfsを選択します。
はい、を押します。
Less vertices...を選択します。
頂点数は15000にします。
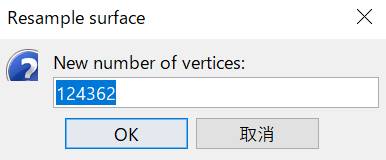
OKを押します。

脳磁図データの読み込み
脳磁図データを読み込みます。Functional dataをクリックします。
akiraを右クリックしReview raw fileを選び、脳磁図ファイルを選択します。
なんか絵が出てきます。
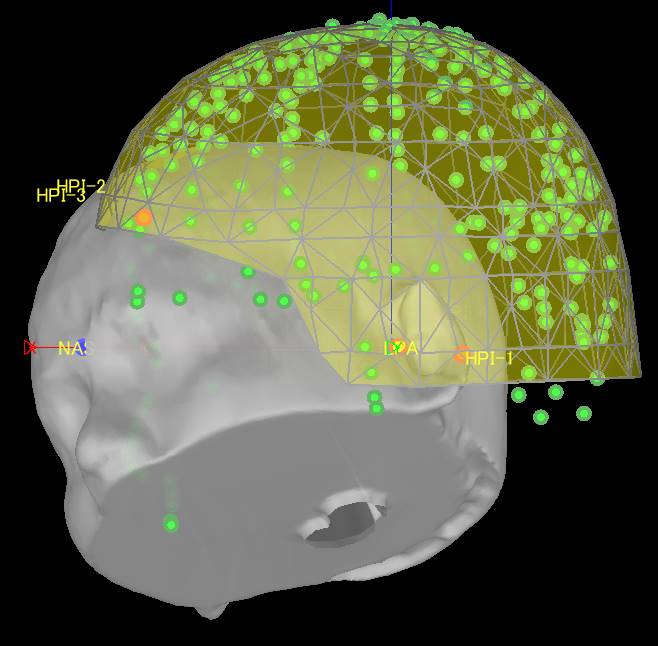
後で直すことにします。いいえを押します。
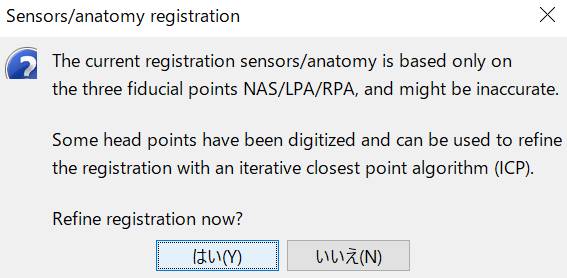
OKを押します。
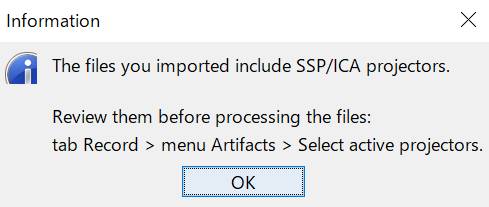
SSPは全部かけることにします。チェックを入れるときエラーと音が出るかもしれませんが、無視します。
最後にSaveを押します。
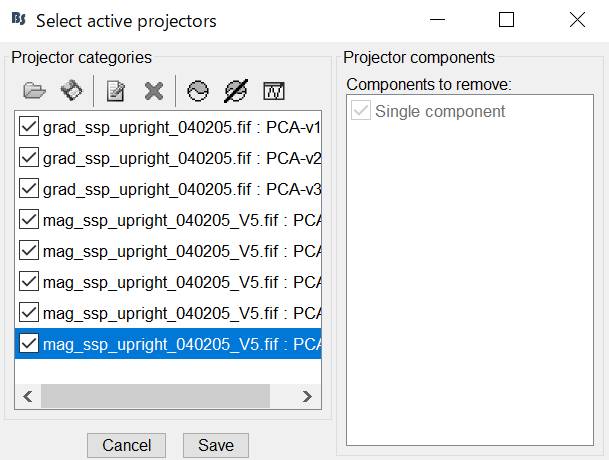
SSPがかかっていることを確認します。この過程は省いてもかまいません。
わかりやすいmagnetometerで見てみます。
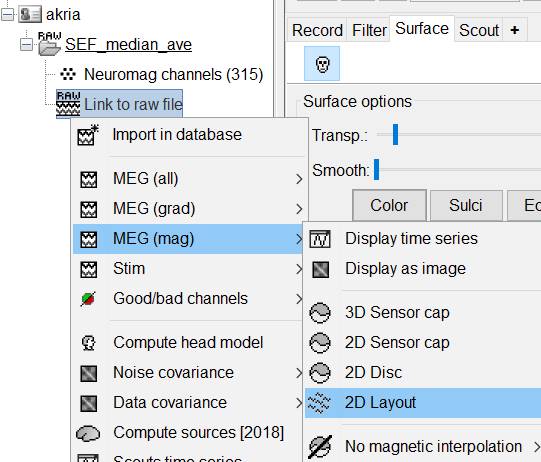
ちゃんとSSPはかかってみたいです。
Neuromag channels (315)を右クリックしてMRI registration→Refine using head pointsを押します。
次にNeuromag channels (315)を右クリックしてMRI registration→Editを押します。
X軸Y軸Z軸が通常と異なっていますが微調整し、OKを押します。

はいを押します。
いざ電流源推定
Compute head modelを選択します。
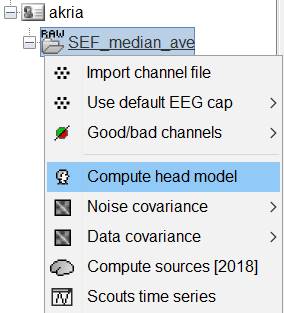
OKを押します。
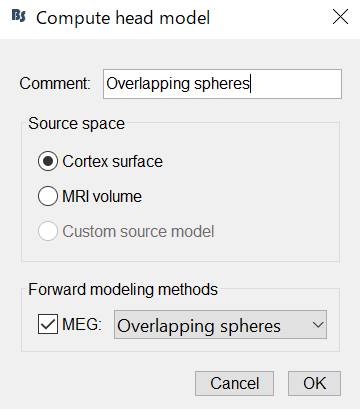
baselineや bandpassフィルタは無視して、とりあえず雑音行列を作成します。
Noise covariance→Compute from recordingsを選択します。
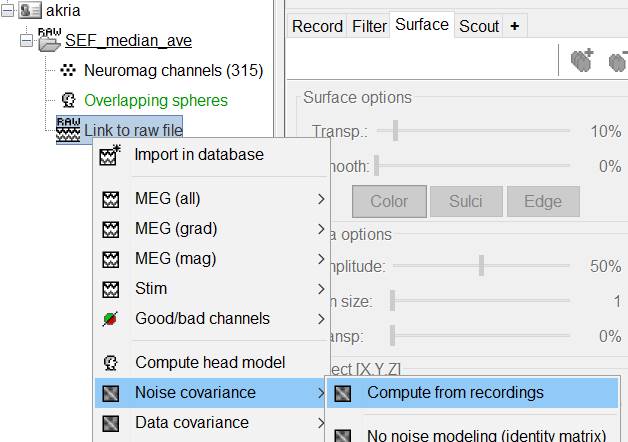
OKを押します。
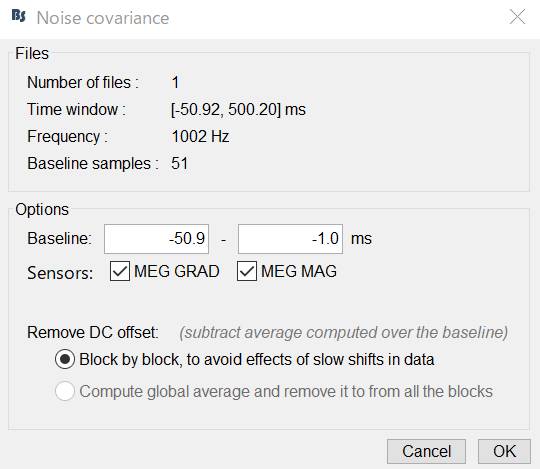
Compute souroces [2018]を選択します。
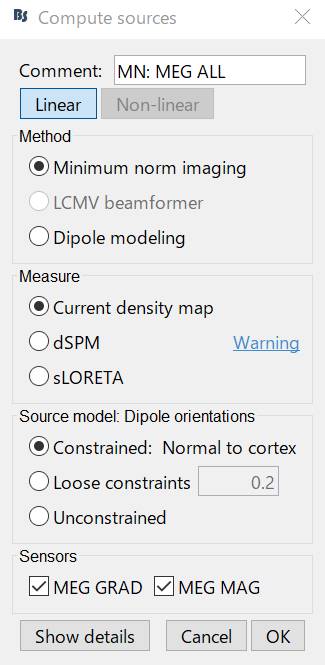
OKを押します。
Link to raw fileの下のMNE_MEGALL云々を右クリックしてCortical activations→Display on cortexを選択します。

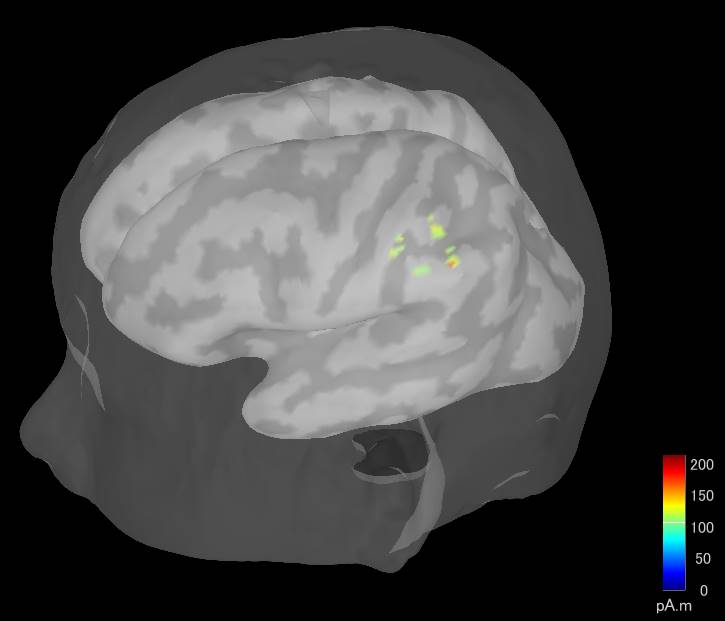
23msecの時の推定結果です。scalpも一緒に表示させています。