9.
ポリゴンメッシュ化
3D Source Reconstr.をクリックします。
Loadをクリックします。
MAT化された脳磁図データを選択し、Doneをクリックします。
適当に名前を付け、OKをクリックします。
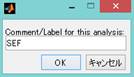
MRIをクリックします。
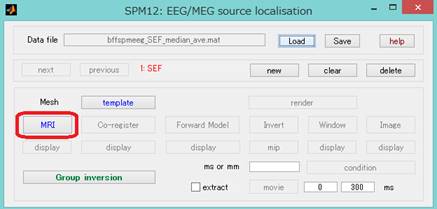
NIfTIファイル化した構造画像を選択し、Doneをクリックします。
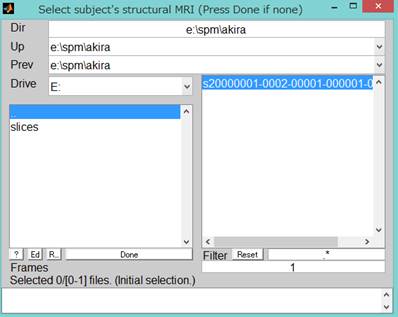
normalを選択します。
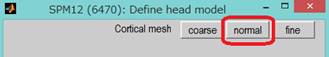
少し時間がかかります。Core i7 4750-HQで約5分かかりました。
結果が表示されます。
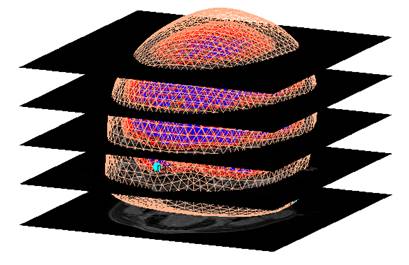
ちゃんと皮髄境界を抽出できてるか見てみました。
set(gcf,'resize','on');
hs=findobj(gcf,'type','surface');
hp=findobj(gcf,'type','patch');
set(hs,'visible','on');
set(hp,'visible','on');
set(hs([2,3,4,5]),'visible','off');
set(hp([1,2,3]),'visible','off');
set(hp(4),'facecolor','none');
view([0,90]);
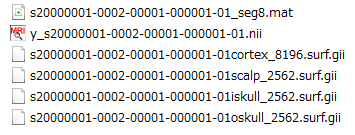
また****_seg8.mat、y_****.nii、****cortex_8196.surf.gii、****scalp_2562.surf.gii、****skull_2562.surf.gii、oskull_2562.surf.giiという5つのファイルが作成されました。
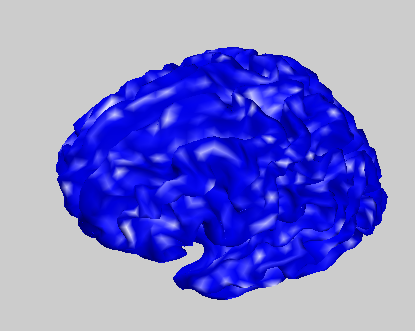
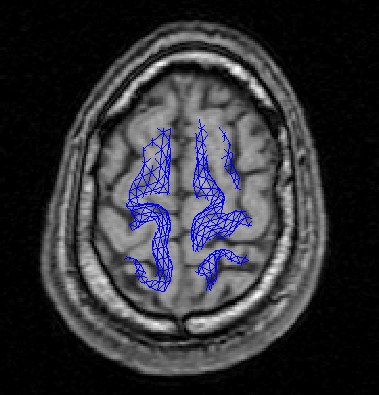
giiというのはGIfTIファイルです。以下のようなコードで皮質のメッシュを確認できます。
filename='s20000001-0002-00001-000001-01cortex_8196.surf.gii';
cortex=gifti(filename);
figure;plot(cortex);
rotate3d on;